查询某一字段值的长度_MetaCyc数据库学习笔记——简介及查询方法
一、简介BioCyc是一个含有16,822途径/基因组的数据库(Pathway/Genome Databases, 简称PGDBs)。BioCyc数据库中涉及细菌、古细菌、酵母、果蝇、小鼠和人类。而BioCyc数据库又可进一步被分成三级:第一级:数据库至少有1人年的科学实验文献管理且是最准确的。MetaCyc属于这一级,具有20人年以上的管理。第二级和第三级:数据库包含代谢途径的计算预测、代谢途径

一、简介
BioCyc是一个含有16,822途径/基因组的数据库(Pathway/Genome Databases, 简称PGDBs)。BioCyc数据库中涉及细菌、古细菌、酵母、果蝇、小鼠和人类。而BioCyc数据库又可进一步被分成三级:
第一级:数据库至少有1人年的科学实验文献管理且是最准确的。MetaCyc属于这一级,具有20人年以上的管理。

第二级和第三级:数据库包含代谢途径的计算预测、代谢途径中编码缺失酶的基因的预测和操纵子的预测。
MetaCyc是一个非冗余的、具有经过实验阐明的代谢途径和酶的数据库。MetaCyc数据库包括以下内容:
· 存储的代谢途径涉及初级代谢和次级代谢
· 存储了代谢物、酶、酶复合体和途径相关的基因
· 外部链接到包含蛋白和核酸测序数据、文献数据和蛋白质结构等其他生物学数据库
· 与EcoCyc相比,提供的基因组数据较少
二、应用
MetaCyc主要可被用于以下四个方面:
1)用于基于计算的代谢重构和建模
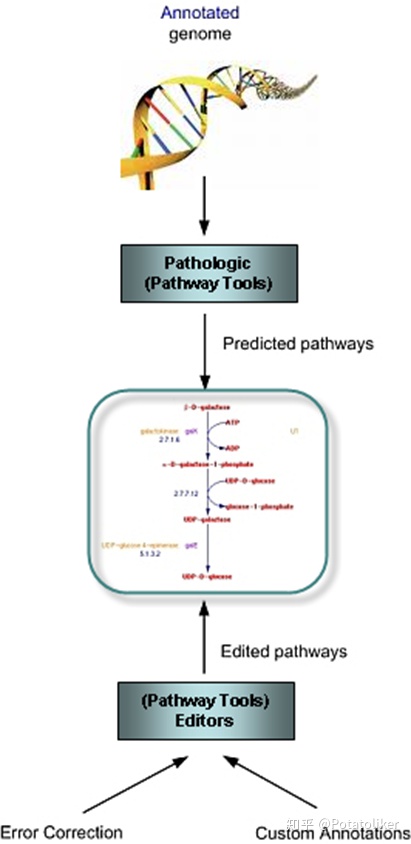
例如,基于MetaCyc数据库,运用Pathway Tools中的PathoLogic从一个生物已知的基因组注释来预测代谢网络。因为代谢网络是通过计算预测所得出的,所以还需要利用Pathway Tools所提供的编辑工具来快速修复错误并自定义注释,并将自定义注释(包括手动生成的注释)添加到储存库。重构的代谢网络可进一步利用Pathway Tools的MetaFlux将其转换为代谢模型。
2)支持代谢工程及药物靶点的开发
代谢工程在很大程度上依赖于对代谢途径的了解、良好特性酶的获取及其编码基因的可用性,而MetaCyc能够为之提供丰富的代谢途径和酶数据库。此外,代谢途径的信息可以用于药物靶点的开发和药物基因组学。
3)代谢物数据库辅助的代谢组学研究
MetaCyc提供了有关代谢物、代谢反应和酶的大量数据,可以为生物合成的潜在途径或给定代谢物的代谢提供见解。
4)可作为有关代谢途径和酶的百科全书
可以用于比较不同生物体之间的代谢途径。
三、查询方法
MetaCyc中的代谢途径、蛋白质、反应及代谢物可以通过以下三种方式进行查询:
1)基于文本的查询
这种方法可以用于对名称未知的对象进行查询
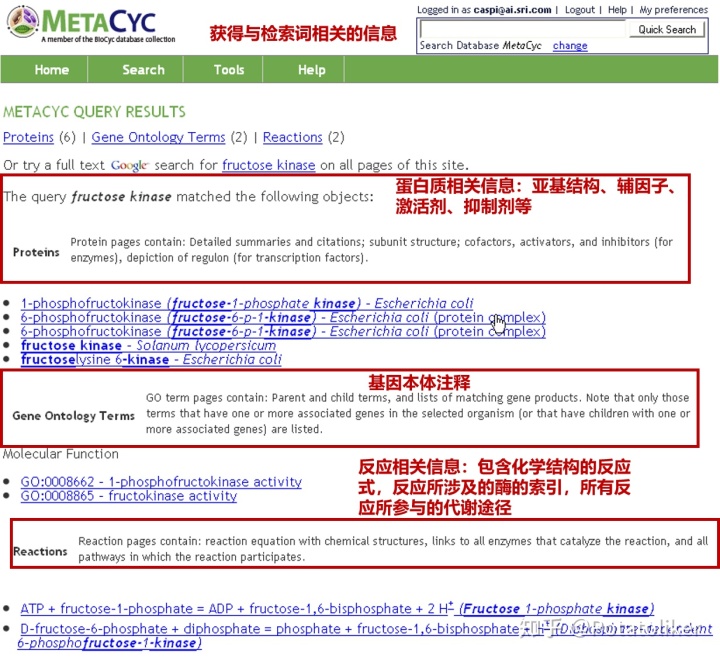
例如:查询与6-磷酸果糖激酶(6-phosphofructokinase)相关的信息,但是忘记了6-phosphofructokinase这一确切的名称。
step1:在页面右上角的Quick Search搜索框输入关键词frutose kinase进行检索

step2:查看关键词检索后的详细信息
2)使用标识符直接进行查询
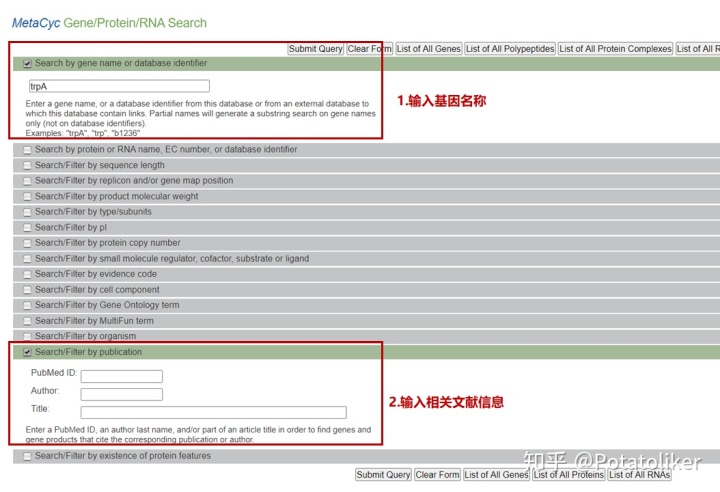
可直接通过检索基因、蛋白质、RNA、化合物、反应、代谢途径及生长的培养基进行查询,通过链接进入后,还可以进一步设置查询的条件。

例如:搜索某一文献中所利用的基因的相关信息。在搜索页面对搜索条件(如:序列长度、宿主、文献等等)进一步限制,可以使得搜索结果更为准确。
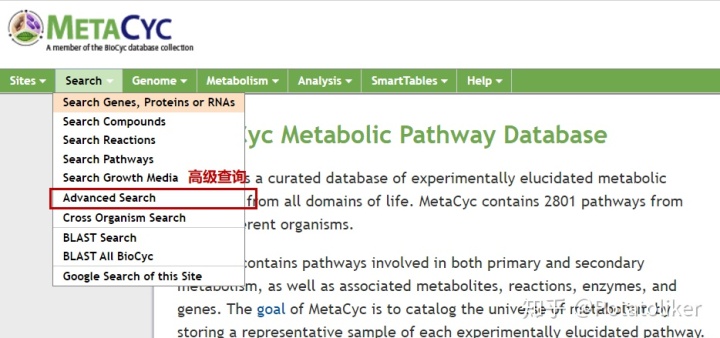
3)高级查询
高级查询通过对查询进行编辑,实现从Pathway Tools服务器上托管的PGDB中提取数据。即通过对数据字段值的约束、组合来自数据库不同区域的信息以及对数据字段进行操作,从而实现PGDB中选择数据子集。
而查询界面可分为以下两种:
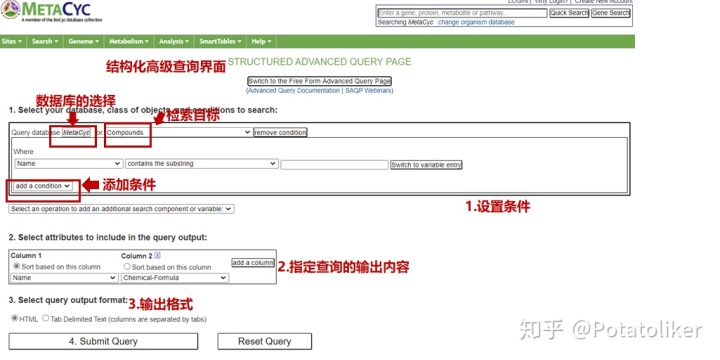
· 结构化高级查询界面
该查询界面无需了解基础查询语言(BioVelo)即可进行查询。当设置多个条件时,可利用逻辑运算符和、或、或非、与非来确定不同条件间的关系。输出格式中HTML为大多数用户选择的格式,而Tab Delimited Text格式则是创建了一个列由制表符所分隔的文本格式的表。
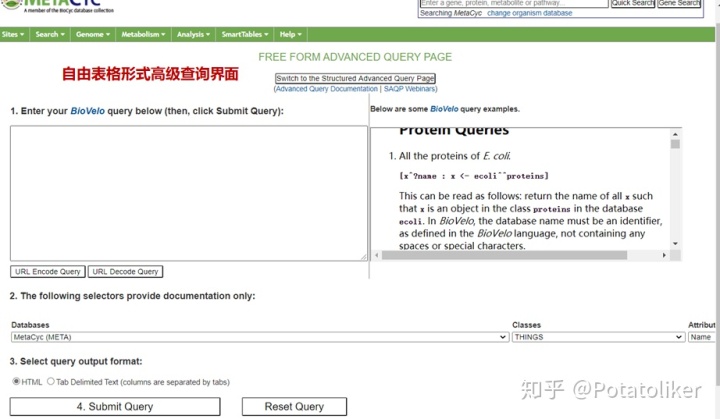
· 自由表格形式高级查询界面
该查询界面提供对BioVelo语言的完全访问,因此它的使用需要了解BioVelo语言的基本语法,相较于前一种方法也更复杂。具体语法内容可参考:https://metacyc.org/bioveloLanguage.shtml。

DAMO开发者矩阵,由阿里巴巴达摩院和中国互联网协会联合发起,致力于探讨最前沿的技术趋势与应用成果,搭建高质量的交流与分享平台,推动技术创新与产业应用链接,围绕“人工智能与新型计算”构建开放共享的开发者生态。
更多推荐
 已为社区贡献1条内容
已为社区贡献1条内容






所有评论(0)